TEXTO DO CANAL BRASIL SEM ALERGIA NO YOUTUBE
Clique aqui para assistir o vídeo no YouTube
O texto pode conter erros na transcrição uma vez que são geradas automaticamente pelo YouTube. Não deixe de assistir o vídeo em nosso canal.
3:44 esqueceram 4:27 boa noite da espada jacksonville uh é uma grande honra ouvir o seu 4:32 palavras sobre crispr este nascimento ii poderia dizer crispr 4:39 é um capítulo intrigante da medicina é um capítulo intrigante da vida 4:47 e ii tenho certeza que isso admite que você será bem sucedido e 4:55 eu gostaria de agradecer a você e ao dr rabio lanot por aceitarem o convite 5:04 agora vou compartilhar minha tela para começar minha palestra 5:36 esqueceram 6:23 [Música] 6:32 esqueceram 6:39 [Música] 7:09 [Música] 7:42 um 8:18 [Música] 9:03 [Música] 9:17 [Música] estrangeira 9:53 [Música] 10:29 [Música] 11:40 uh 12:06 [Música] 12:36 é 13:32 uma 15:34 [Música] 16:04 [Risada] 17:02 esqueceram 17:59 é 18:08 [Música] 19:18 [Música] 20:18 um 20:39 [Música] 20:46 comece seu discurso bem vindo ao simpósio obrigado pelo convite 20:54 deixe-me começar minha apresentação 21:00 trabalho de pesquisa usando a tecnologia crispr cast 9 21:09 a apresentação de hoje será dividida em parte primeiro apresentarei o uso do 21:15 tecnologia crispr cas9 para tratar a doença estável do ferro e minha pós-graduação 21:20 a aluna gabrielle lamont apresentará todos os derivados do crispr cas9 21:25 tecnologia pode ser usada para detectar infecção viral 21:32 a palavra crispr significa repetições de penetração curta no interespaço regulatório agrupado 21:41 A tecnologia do sussurro cas9 é derivada de pesquisas sobre bactérias, foi descoberta inicialmente em 2005 21:49 que a sequência crispr continha sequência viral e ainda havia uma 21:54 hipótese de que crispr cas9 é o sistema imunológico bacteriano 22:00 foi só em 2013 que se descobriu que o crispr cas9 22:06 pode ser usado para induzir modificação específica do genoma humano 22:11 e isso começou uma grande explosão de artificial 22:17 na verdade, o sistema de fundição crispr é usado por bactérias para matar bacteriófago bacteriófago são 22:24 extremamente abundantes são dez vezes mais abundantes em bactérias e há uma guerra em curso entre 22:32 bactérias e bacteriófagos há milhões de anos 22:39 foi inicialmente descoberto que eles estão na área do genoma sequência repetida constante 22:47 pesquisadores estavam se perguntando para que serviam essas sequências repetidas e então descobriram que o 22:54 sequência entre uma repetição constante foram sequenciados que vieram do genoma de vários 23:01 bacteriófago na verdade o que normalmente acontece é quando um 23:07 Bactérias infectadas por bacteriófagos normalmente a bactéria do vento bacteriano está morta 23:13 mas às vezes você tem um vírus defeituoso que infecta sem matar as bactérias, mas eles então 23:19 ser capaz de adquirir alguma parte da sequência do vírus 23:24 e ele armazenará isso em seu genoma e estará pronto quando precisar desse bacteriófago novamente 23:31 no futuro a partir do DNA nas bactérias da área crispr 23:37 irá primeiro expressar o pó pré-cr e depois haverá um complexo que será feito entre 23:43 rastreador ou crna e a proteína de ferro fundido 23:49 este complexo de proteína rna crna cas9 atacante se ligará às bactérias de hdna 23:57 e induzir um corte do dna do bacteriófago para essencialmente matar o vírus 24:07 para se ligar ao dna a proteína cas9 requer a presença do espaçador total 24:12 motivo adjacente que é simplesmente njj para esses streptococcus pyrogene 24:19 caminho, então há um crrna 24:24 que contêm uma sequência variável de 20 nucleotídeos que será 24:30 complementar à sequência do bacteriófago e depois há também o rastreador rna que é uma constante 24:36 sequência de rna que forma um complexo com o crm quando as três partes estão juntas cr rna 24:44 rastreador ou uma proteína de ferro fundido, um corte será induzido em exatamente três 24:50 apertado da planta, é claro, já que esta é uma guerra, há 24:56 medida de contorno que são tomadas pelo fago eles irão mutar seu genoma para que eles se tornem 25:02 resistente não reconhecido pelo crrna e sobreviverá 25:08 defesa bacteriana o crispr cas9 big bang começou em 2012 25:17 quando a geração x e colegas perceberam que a tecnologia crisper cast 9 pode permitir 25:23 cortam o genoma de planetas e animais eles também fundem seu cr rna e o rastreador rna 25:31 juntos para formar um único guia rna isso foi feito essencialmente porque 25:38 o único guia rna é algo que pode ser patenteado enquanto o crn no rastreador 25:44 sendo naturais não podem ser patenteados 25:50 durante o ano seguinte, houve uma explosão de artigos confirmando que o casino crisper 25:56 tecnologia pode ser usada para cortar o genoma de bactérias células humanas carbono animal rato drogas 26:02 planta peixe-zebra voa nematóides macacos 26:10 muitos desses artigos foram publicados em revistas de prestígio como a Nature 26:15 ciência natureza biotecnologia célula molecular célula molecular 26:23 houve uma rápida explosão de artigo e, como você pode ver, em 26 de novembro de 2020 26:31 21 420 artigos foram publicados onde a palavra crispr é mencionada 26:40 a principal razão desta rápida explosão de artigos é que custa muito menos derivar 26:47 uma sequência que será capaz de cortar uma sequência específica do genoma em comparação com outras 26:53 tecnologia pré-existente, como proteína de dedo de zinco e alfaiates 27:00 como mencionado antes da ligação da proteína cas9 ao dna 27:06 exigir a presença de um espaçador de foto adjacente ao pam no local que é njj para o cas9 derivado 27:12 da biologia do estreptococo há então a ligação também do 27:18 rna guia único que reconhecerá a sequência de 20 nucleotídeos 27:24 e quando o complexo é feito entre a proteína cas9 o rna guia único e o dna lá 27:31 é um corte que será feito a exatamente três nucleotídeos da panela 27:39 uma vez dentro do núcleo, o complexo resultante travará em uma sequência curta conhecida como pan 27:46 o cast 9 irá descompactar o dna e combiná-lo com o rna alvo 27:53 se a partida estiver completa, o cas9 usará duas pequenas tesouras moleculares para cortar o 28:00 dna quando isso acontece a célula tenta reparar o corte 28:06 mas o processo de reparo é propenso a erros, levando a mutações que podem desativar o gene, permitindo que os pesquisadores entendam sua 28:14 função essas mutações são aleatórias, mas às vezes os pesquisadores precisam ser mais precisos 28:20 por exemplo, substituindo um gene mutante por uma cópia saudável, isso pode ser feito adicionando outro pedaço 28:27 de DNA que carrega a sequência desejada uma vez que o sistema crispr tenha feito um corte 28:33 este modelo de DNA pode emparelhar com as extremidades cortadas recombinando e substituindo a sequência original pela nova versão 28:46 um dos motivos da rápida explosão é que a tecnologia clássica do cristal também utilizou tudo o que foi desenvolvido pelo gene 28:53 que foram os 30 anos que o precederam temos métodos para entregar o dna 28:59 usando aav e, em seguida, vírus associados polímeros catiônicos lipossomas micro 29:05 operação eletro de injeção todas essas técnicas são usadas no contexto de crispr 29:12 quando uma quebra de fita dupla é produzida no dna, a maioria das quebras será reparada por 29:18 adjacentes não homólogos que levarão a micro deleção ou micro inserção isso é frequentemente 29:26 usado para eliminar a expressão de um gene alterando o quadro de leitura 29:32 e também pode ser reparado por reparo dirigido por homologia que requer a presença do doador 29:37 dna que contém sequência de homologia com o que está retrocedendo o que está seguindo 29:43 o corte e depois entre as duas sequências de homologia há uma sequência em azul 29:49 que pode ser um único nucleotídeo ou um gene inteiro que será inserido ao lado do 29:55 quebra de fita dupla quando usamos o crispr classe 9 30:00 tecnologia pretendemos produzir uma quebra de fita dupla em um local preciso no genoma humano 30:07 no entanto, o elenco 9 pode às vezes induzir corte em outros locais do genoma que são 30:13 chamado software de computador de mutação alvo buff pode prever essas mutações fora do alvo usando 30:20 toda a sequência do genoma humano, porém esses softwares não são perfeitos 30:25 e às vezes eles imprimem a mutação alvo no local onde não há corte 30:31 e às vezes haverá um corte no lado que não é previsto pelo computador 30:39 existem ou no entanto algumas técnicas experimentais, como um método de pilha de guias, que permitem 30:46 para identificar experimentalmente os locais de mutação alvo este guia 30:52 técnica usou a introdução de um oligonucleotídeo curto de 34 pares de bases 30:59 nas laterais dos cortes e posteriormente por pcr o local de inserção pode ser identificado 31:05 sequenciando a presença desses fora do alvo 31:10 mutação é o principal problema que atrasa o uso 31:15 da tecnologia crispr cat9 para correções diretas do veículo 31:23 um dos métodos para reduzir a mutação alvo é simplesmente reduzir em dois ou três o 31:29 número do rna guia único que se liga ao dna alvo 31:39 outro método é usar uma nuclease cas9 mutada que corta apenas uma fita de dna é então 31:46 chamado de caso do joelho há variação de cas9 onde as cáries cortam apenas o 31:53 fita inferior de DNA e outras mutações da classe 9 que permitem cortar apenas a parte superior 32:00 fita de dna é assim possível induzir mais 32:05 quebra de fita dupla precisa no dna usando o cas9 nikkei 32:12 e dois rna guia único, cada um detectando uma sequência de 20 nucleotídeos perto de 32:17 uns aos outros [Música] também é possível usar um 32:23 fusível de nuclease cas9 cas9 não funcional com aquele 32:29 nucleados, então dois rna guia são novamente necessários para detectar sequências que estão próximas 32:36 outro e o sapo uma nuclease precisa formar um dímero para poder 32:41 para cortar o dna finalmente alguns pesquisadores sofreram mutação 32:49 o gene que codifica a partir do elenco 9. eles modificaram alguma sequência que codifica para amino 32:57 ácido para reduzir a ligação não específica entre o cas9 e o dna 33:06 o gene sp cas9 é muito grande para ser inserido com um único rna guia dentro de um adeno 33:13 vírus associado e, portanto, os pesquisadores identificaram cas9 de 33:18 outras bactérias que são menores por exemplo o estafilococo é menor que o sp 33:27 9 mas tem um caminho diferente que é mais restritivo 33:33 outro tipo de enzima crispr cas9 foi identificado, é chamado de cpf1 33:39 produz cânceres pegajosos é outro corte de sangue do dna 33:46 há apenas uma série inteira de vários valores de contenção cas9 com kylia 33:52 que requerem abas diferentes 33:58 a tecnologia crispr cas9 pode ser usada não apenas para reduzir cortes no dna, mas também 34:04 para induzir a expressão de um gene fundindo cas9 com bp 64 por exemplo 34:10 ou escolhendo cast 9 com caranguejo para corrigir a expressão de um gene 34:18 no meu grupo de pesquisa estamos usando a tecnologia crispr cas9 para desenvolver terapias para várias doenças 34:25 ataxia transversal distrofia muscular de duchenne e doença de alzheimer vou apresentar agora 34:33 inicialmente usamos a tecnologia crispr cas9 para desenvolver um tratamento para fredrich 34:39 ataxia é uma doença de elixir devido à presença 34:44 de um nucleotídeo long try com b gaa no íntron um do gene da fataxina 34:52 esta longa repetição reduz a expressão do gene da fataxina levando a 35:00 problemas neurológicos e cardíacos acabamos de usar o crispr cas9 35:05 tecnologia e gerado guia único rna capaz de cortar no intron 1 antes 35:14 e após a repetição do trinucleotídeo levando à sua remoção e aumentando a expressão da ataxia 35:24 de fato, a remoção da repetição de trinocleotídeos nas células do yga 35:31 modelo de camundongo sr de ataxia fredérica dobrou a expressão de frataxina 35:36 em comparação com as células não tratadas e elevou a expressão de proteção para quase 35:43 o nível normal o gene sp cas9 é muito grande para ser 35:49 entregue com dois rna de guia único por um único aav, estamos usando apenas o menor 35:56 cg cas9 gene para remover a repetição de trinucleotídeos no íntron 1 36:02 do gene da fataxina usando esta nuclease cg cas9 menor 36:10 também somos capazes de remover a repetição de trinucleotídeos no íntron um do gene da frataxina 36:20 também estamos usando a tecnologia crispr cas9 para desenvolver um tratamento para duchenne 36:25 distrofia muscular a distrofia muscular de duchenne é devido a 36:31 mutação em um gene que codifica para a proteína distrofina é um gene grande contendo 79 éxons 36:39 alguns desses éxons não contêm um múltiplo de três nucleotídeos e, portanto, 70% 36:46 dos casos de distrofia muscular de duchenne são devidos à deleção de um ou vários 36:51 exames e o número total de nucleotídeos de codificação que são deletados 36:56 não é um múltiplo de três 37:01 por exemplo nesta apresentação temos uma deleção do exon 50 que não 37:07 contêm um múltiplo de três nucleotídeos, isso leva a uma mudança de quadro 37:12 e haverá um códon de parada no exon 51. 37:18 proteína distrofina é expressa, mas não o final da proteína distrofina 37:24 esta situação pode ser corrigida induzindo o salto que é uma remoção do exon 51 37:32 no rna mensageiro isso é feito usando o nucleotídeo poligonal antisense 37:38 este exame 51 também pode ser excluído induzindo cortes no íntron 50 e 37:46 na frente 51 para remover completamente esse exon, isso resulta 37:52 na expressão do início da proteína distrofina e do fim da proteína distrofina 37:59 mas há, no entanto, uma pequena parte da proteína que está faltando no centro 38:04 da proteína a retirada de um ou vários exames completos 38:11 pode assim restaurar o quadro de leitura e converter um paciente duchene 38:16 em um paciente de Becker, no entanto, alguns pacientes de apoio têm 38:21 sintomas e são obrigados a uma cadeira de rodas aos 11 anos. 38:26 portanto, a melhora de algumas distrofias musculares de duchenne pode não ser significativa 38:35 isso ocorre porque a proteína distrofina tem uma estrutura complexa de fato em sua parte central a distro 38:42 proteína fin contém 24 repetições semelhantes a espectro 38:49 cada espectro como repetição é feito de três hélices alfa hélice a lxb 38:55 e lxc observe que lxa está começando no lado esquerdo e elixi 39:02 está terminando no lado direito e normalmente há uma sucessão de abc abc abc 39:11 o principal problema de deletar o exon completo para restaurar a expressão da proteína distrofina é 39:19 que o início e o fim do espectro como repetição indicado neste esquema pelo preto 39:26 seta não correspondem ao início e ao fim dos exílios e, portanto, ao remover a exaustão completa 39:33 o resultado da estrutura de repetição do tipo espectro pode não ser normal 39:41 paciente com distrofia muscular vetorial tem uma exclusão de um ou vários exames, mas o total 39:48 número de nucleotídeos de codificação que são deletados é um múltiplo de três nucleotídeos e 39:54 portanto, não há mudança de quadro, este é o caso, por exemplo, do paciente Becker ter uma exclusão do exame 40:00 45 a 47 ou com exclusão de 45 a 49 40:06 em ambos os casos não há mudança de quadro no início e no fim da proteína distrofina 40:12 são expressos, no entanto, no local de junção entre os códons restantes, há um 40:20 estrutura da proteína distrofina e devido a esta estrutura anormal da proteína distrofina 40:26 esses pacientes vetores são vinculados a uma cadeira de rodas em tenra idade 40:35 anoitecer no meu grupo de pesquisa em vez de tentar restaurar o quadro de leitura normal 40:41 excluindo exons completos, visamos produzir exames de habilitação 40:47 5054, que não apenas restaurou um quadro de leitura normal, mas também codifica uma proteína distópica com um 40:55 estrutura normal, fizemos nossos experimentos iniciais usando o mioblasto de um 41:01 paciente duchenne tendo uma exclusão do exame 51 52 e 53. 41:08 o número de nucleotídeos de codificação não era um múltiplo de três havia um códon de passo no exon 54 41:16 devido à mudança de quadro, acabamos de usar a tecnologia crisper cast 9 para induzir um corte no exon 50 e um corte no 41:24 exon 54 para criar o ebrate exon 5054 41:31 para produzir este exemplo implicado identificamos inicialmente quais são os possíveis sp cas9 41:39 pan ou quais são os locais onde podemos cortar no exon 50 e no exon 54 41:45 identificamos 10 vezes locais no exon 50 e 14 tamanhos diferentes de pan no exon 53 41:54 esta tabela prevê quais são os resultados da indução de cortes no exame 50 42:01 e no exame 54. quando temos um quadrado azul significa que o 42:09 corte foi produzido no exon 50 logo após os três nucleotídeos e 42:15 pede um aminoácido e o corte foi produzido no exon 54 42:22 logo antes dos três nucleotídeos que codificam um aminoácido, portanto, no ponto de junção, temos o amino 42:29 ácidos que são um escoltado pelo exon 54 seguido imediatamente por um aminoácido 42:36 codificado por exemplo, não há mudança de quadro e não há novo aminoácido 42:43 porém quando a praça está limpa isso significa que temos no entroncamento 42:50 local um novo aminoácido que é produzido porque estamos presos no exon 50 42:56 logo após um dos nucleotídeos de um códon e os dois nucleotídeos que irão 43:01 completar esses códons são do exemplo antes de cortarmos 43:06 logo após um nucleotídeo do códon no éxon 54 e, portanto, os dois primeiros 43:12 nucleotídeos deixados para criar um novo códon no sítio de junção, há assim um novo 43:19 aminoácido no sítio de junção, mas não há mudança de quadro e todos os outros aminoácidos são os 43:26 corretas também é possível neste quadrado em 43:31 vermelho para ter um novo códon produzido no local de junção 43:36 mas este novo códon é um códon de parada isso não é real, queremos fazer todos os quadrados de largura porque 43:44 há uma mudança de quadro que estamos cortando após um nucleotídeo de um códon no exon 15 43:50 e estamos cortando antes do último nucleotídeo de um resfriamento no exon 54 e, assim, adicionamos a junção 43:58 lado há um novo códon que é feito porque há uma mudança de quadro e todos 44:04 os aminoácidos a seguir não são os corretos 44:10 temos testadores de poeira vários pares de ironia guia uma ironia guia cortando na zona 50 44:17 e o outro corte de rna guia no exon 54 acabou de produzir um exame ibrit 1554 44:24 que tinha o tamanho previsto para este exame híbrido, observe que quando 44:31 estamos fazendo cortes no exame 50 e no exame 54 em uma distrofina normal estamos excluindo 44:39 160 000 pares de bases e apesar disso a junção entre 44:45 exon 50 e 54 é do tamanho previsto 44:52 sequenciamos este exame híbrido que foi produzido por corte no exon 50 e 44:58 no exon 54. não apenas o exame eblid era exatamente do tamanho 45:05 previsto, mas a sequência também foi exatamente tão preditiva 45:10 por exemplo, tivemos um local de junção das fusões do exon 50 no exame 54 produzindo 45:19 exatamente o aminoácido previsto, também obtemos no sítio de junção um novo códon 45:27 codificação para o aminoácido previsto ou codificação para um códon de parada e 45:33 em algum momento, como previsto pelo quadrado branco, tivemos uma mudança de quadro e quando houve 45:39 uma mudança de quadro, havia códons de parada que se destinavam aos exílios liberais resultantes 45:50 como mencionado anteriormente a proteína distrofina contida em sua parte central 45:56 24 espectros como repetir cada um sendo feito de três alfa-hélices ab e c 46:03 acabamos de usar um guia rna para induzir um corte no exon 50 em uma sequência de codificação 46:10 para lxc e outro guia rna induzindo um corte no exon 54 46:15 também em uma sequência que codifica para a hélice c o exon evidente resultante 5054 46:22 pede um ibrim elixi onde o início de nxc 46:29 é codificado pelo exon 50 e o final do elixi é codificado pelo exon 54. 46:36 esta é uma estrutura que foi prevista por computador usando a sequência do resultado 46:42 proteína quando o biovidro desta duchenne 46:48 paciente com deleção do exon 51-53 são fundidos para formar alguns pequenos 46:55 fibras musculares e cultura chamadas miotubos, na verdade, essas fibras musculares não expressam distrofina porque 47:02 este é um paciente de duchenne no entanto o mioblasto de um humano saudável 47:07 quando se fundem formam um pequeno biotubo e expressam este tópico como pode ser visto aqui neste Western 47:14 sangue quando utilizamos o bioblasto do paciente duchenne e induzimos a formação do 47:21 zona ignitiva 5054 temos expressão da proteína distópica em cultura 47:27 e como você pode ver esta proteína distrofina tem um peso molecular menor do que o normal 47:33 distrofina porque há deleção do exon 51 a 53 47:39 e uma deleção adicional de parte do exon 50 e parte do exame 54. 47:45 parte da proteína distrofina que está ausente é por isso que a proteína é 47:51 menor, mas, no entanto, é expresso 47:56 para nossos experimentos individuais iniciais, usamos o modelo de mouse html 48:02 este é um camundongo transgênico que expressa o gene da distrofina humana 48:08 todos os íntrons e todos os éxons que eletroporamos no músculo de 48:14 este revestimento de plasmídeo de camundongo para os combustíveis sp cas9 com a proteína verde fluorescente 48:21 e dois rnas de guia único isso um mês depois quando tiramos o músculo 48:28 houve expressão da proteína verde fluorescente confirmando que o plasmídeo foi 48:36 eletroporado corretamente nas fibras musculares levando à expressão do 48:41 proteína verde fluorescente e provavelmente também levando à expressão do sp ferro fundido 48:47 e depois de duas passadas de guia extraímos o dna dessas 48:55 músculo e primeiro confirmamos usando um teste chamado de enzima 49:01 mas, de fato, eles estavam sendo constantemente produzidos no exon 50 e 54. 49:08 use pcr para amplificar a zona eblatex 5054. 49:14 observe que nos músculos que não são tratados com a tecnologia crystal classe 9 49:19 não há amplificação do exemplo 5054 porque há 160.000 pares de bases 49:26 entre esses dois exilados e, portanto, as duas cartilhas para o pcr são demais 49:33 separados um do outro 49:43 nós então sequenciamos este exon 1554 que foi produzido in vivo 49:50 no músculo do camundongo expressando o gene da distrofina humana e como previsto tivemos a sequência de 49:57 exon 50 e um novo códon no lado da junção 50:03 seguido por todos os códons corretos que codificam para o aminoácido normal no exon 50:09 54. isso é exatamente como previsto in vivo 50:17 no entanto, para a entrega do gene cast 9 no mal para vários músculos 50:24 precisamos usar um vírus adeno associado como mencionado antes do sp cas9 50:31 gene é muito grande para ser entregue com dois rna guia por um único aav e, portanto, usamos para 50:38 nossos próximos experimentos a faca fundida do staphylococcus moleus que é um cas menor que 50:46 permitir a entrega com ironia de dois guias por um único avp neste caso usamos uh 50:55 guia rna que induziu cortes no exame 47 em uma sequência de codificação para 51:01 lxb e no exon 58 em uma sequência novamente codificando para elix b 51:08 isso resultou na formação de um exame de ebola 51:13 4758 codificação para um lxb ibrigid que tem uma estrutura normal 51:19 o começo do exp ser codificado pelo exon 47 e o fim desse mal 51:27 Philips estar sendo codificado pelo exon 58 51:34 então usamos para nosso experimento imbibo um novo modelo de mouse chamado hdmd delta 52 51:43 é o mesmo modelo de camundongo anterior que contém o gene da distrofina com todos os 51:50 éxons e todos os íntrons, exceto que este camundongo tem uma deleção do exon 52 e, portanto, 51:57 não há expressão do gene disfórico humano acabamos de usar o crispr classe 9 52:03 tecnologia para induzir um corte no exot 47 e um corte no exame 58 52:09 produzindo o exame de ibrina 4758 resultando na produção de um 52:15 proteína distrofina contendo um exame mal a cada lxp 52:26 injetamos neste mouse hdmd delta 52 52:31 aevs codificação para sc 9 e 2 guia único rna um mês depois observamos no músculo 52:39 a expressão do gene da distrofina humana, incluindo no coração 52:47 estamos apenas propondo um tratamento da distrofia muscular de duchenne que seria a entrega sistêmica por 52:53 um vírus adeno-associado do gene da classe 9 e de dois rna guia 52:59 para formar qualquer exame de pão em contraste com o salto de exon, que é um tratamento 53:05 feito ao nível do mensageiro rna o tratamento que propomos ao nível do dna seria 53:12 permanente a tecnologia crispr cas9 está evoluindo rapidamente 53:18 e novas tecnologias derivadas do crispr cas9 permitem agora a modificação de um único 53:26 nucleotídeo mais de 32.000 nucleotídeo único 53:32 modificações são responsáveis pela doença estável precoce e, portanto, a 53:38 capacidade de corrigir um único nucleotídeo forneceria tratamento para 53:44 a maioria destes curando doença estável o primeiro tratamento que permite a 53:50 modificação de um único nucleotídeo foi desenvolvida por kamal em 2017 que usa 53:58 um cas9 nikkei que é o cast 9 modificado que é capaz de cortar apenas um 54:04 filamento de dna e este estojo fundido 90 é fundido com 54:09 acetaminofeno esta tecnologia é permanente para 54:15 modificar clinicamente o city bean em um uvd que é substituído 54:21 por um tempo no dna 54:26 a principal limitação dessa técnica é a modificação química da cidade 54:32 ocorrerá em uma janela estreita localizada em 12 a 16 pares de bases do 54:40 ngg pan usamos inicialmente a edição base 54:48 tecnologia para desenvolver um tratamento para a doença de Alzheimer 54:57 a doença de Alzheimer é produzida por um metabolismo anormal da munição 55:04 proteína normalmente esta proteína é cortada pelos secretários alfa 55:10 seguido por um corte pela célula gama estas proteínas peptídeos e proteínas 55:16 fragmentos que são degradados sem causar problemas, porém esta proteína também pode ser cortada por 55:24 a sequência beta seguida por um corte pelas sequências gama e isso produziu 55:30 infecções curtas de 40 42 aminoácidos beta amigo longo que se agregam a 55:37 uns aos outros formando aminoácidos que interferem na transmissão sináptica 55:44 levando à morte do neurônio e os problemas de memória 55:50 este esquema ilustra a sequência de aminoácidos da parte transmembrana do 55:56 proteína repressora anaeróbica podemos ver a posição do beta alfa 56:02 e gama separa calcita todos os aminoácidos na estrela acima 56:08 seus principais são aminoácidos que são modificados levando a 56:13 família ou forma da doença de alzheimer, por favor, observe a posição com a seta vermelha esta é a alanina 56:20 na versão 673 quando esta adenina é alterada por vale 56:25 isso leva a doença de Alzheimer de início precoce grave e você 56:30 são um zemer aos 40 anos. no entanto, quando esta adenina é alterada por uma viagem 56:37 você não é alzheimer mesmo quando tem 95 105 anos como mostrado por johnson nepal na natureza 56:44 2012. 56:49 a presença da mutação a673t também conhecida como a mutação islandesa 56:57 reduzir a secreção de mutação de um beta 40 em nosso peptídeo de qualidade de dados 57:02 para o appg do tipo selvagem e para appg contendo a mutação london 57:12 nossos experimentos mostraram que a presença da mutação h673t 57:20 reduzir a secreção de um peptídeo beta 40 e beta 42 pelo epp 57:27 genes não apenas para o gene do tipo selvagem, mas também para genes app contendo vários genes familiares. 57:34 Mutações da doença de Alzheimer 57:41 como mencionado antes, a tecnologia de edição base crispr cas9 permite modificar 57:48 o reitor da cidade em um momento 57:55 acabamos de usar a tecnologia de edição básica para direcionar o citoplano no 58:03 fita antecedente do códon de alanina transformando essa citodina em um 58:09 e apenas mudando o códon de alanina em um triângulo 58:18 o principal problema com esta abordagem é que, embora queiramos modificar a citodina 58:24 na fita decente do códon de adenina existem outros nucleotídeos de acidez 58:32 próximos que também são afetados pela abordagem de edição básica 58:40 construímos 14 enzimas de edição de base diferentes para poder quantificar 58:47 mais especificamente 58:56 modificando a cidade e o códon anti-sentido de led, conseguimos introduzir 59:05 mutação em até 17 do avpg porém outra acidez 59:13 também localizados na vertente antecedente também foram modificados pelo sujeito 59:22 uma nova tecnologia fantástica chamada privacidade foi recentemente desenvolvida por lápis sobre 59:28 topo com licenças em princípio 59:38 a tecnologia de edição principal usa um novo fusível de caixa cas9 com 59:44 uma transcriptase reversa também requer um guia de edição principal conhecido 59:51 como um porco rs 59:57 o rna do porco é essencialmente um rna guia único prolongado, portanto, tem um único guia 1:00:04 rna contém uma sequência espaçadora que reage com 20 nucleotídeos 1:00:11 no dna de destino, ele também contém o andaime constante do único 1:00:17 guia rna que está em vermelho e depois no seu 1:00:22 cinco extremidade prime há um prolongamento com o lado de flexão do primer que é um 1:00:28 sequência de 10 a 17 nucleotídeos reagindo com a parte superior 1:00:33 fita de dna que é seguida pelo molde da transcriptase reversa 1:00:39 novamente, que tem 10 a 17 nucleotídeos de comprimento e que conterá alguns 1:00:46 nucleotídeo em vermelho neste caso indicando qual nucleotídeo 1:00:52 tem que ser modificado pelos transcriptivos reversos 1:00:59 um plasmídeo desenhado por anzalo natal 1:01:04 está disponível no edgy para construir um novo peg rna 1:01:14 este plasmídeo continha um gene de proteína fluorescente vermelho que pode ser removido por cortes bsa1 que 1:01:21 produzir uma espinha dorsal da proteína e, em seguida, os outros componentes são o primer espaçador que liga o lado inverso 1:01:27 modelo de transcriptase e o couro cabeludo de RNA de porco, todas essas sequências são únicas 1:01:33 nucleotídeo poligonal encalhado que pode ser adquirido da idt essas quatro partes são então montadas 1:01:40 juntos para produzir uma nova garantia de pagamento 1:01:46 para usar a tecnologia de edição principal, primeiro temos que identificar a guia positiva adjacente ao espaçador de fotos 1:01:54 que é njj para a classe nove de streptococcus pyrogene 1:02:00 isso permitirá que o cas9 se ligue ao dna, então a sequência espaçadora do peg rna 1:02:07 se ligará a uma sequência de 20 nucleotídeos de dna, neste caso a fita inferior e a formação do 1:02:14 complexo entre o peg rna classe 9 décadas e 1:02:19 o dna induzirá o corte a exatamente 3 nucleotídeos do caminho 1:02:25 na fita superior de dna, isso liberará a fita superior de dna para poder 1:02:33 interagir com o primer de ligação do lado da pilha o peg rna e depois o inverso 1:02:39 molde de transcriptase que continha alguns nucleotídeos a serem mutados estará disponível para o 1:02:47 transcriptase reversa para sintetizar um novo DNA 1:02:52 força superior significa distrofia muscular de duchenne 1:02:59 paciente tem uma parada chamada no dmdg pois não tivemos 1:03:05 acesso às células do paciente contendo tal apontamento decidimos introduzir 1:03:12 esses códons de parada usando a tecnologia de edição principal, então em cada caso tivemos que identificar 1:03:19 um ngg pam identifica a sequência do espaçador de fotos peg rna e, em seguida, 1:03:27 modificar o modelo de transcriptase reversa para entrar para modificar o 1:03:33 códon para um aminoácido em um códon de parada neste caso nós mudamos 1:03:41 acetaminofeno para introduzir o material tga 1:03:50 usamos com sucesso essa abordagem para apresentar os acionistas no exame 9 20 35 1:03:57 42 55 e 61. 1:04:04 acabamos de projetar vários peg rna direcionados ao dmd exon 35, como você pode ver, 1:04:12 variou o molde da transcriptase reversa em azul de 10 a 16 nucleotídeos 1:04:20 e também variamos o sítio de ligação primária em verde de 10 a 15 nucleotídeos 1:04:27 e no local de mutação desejado que introduzimos em 1:04:34 introduzir essa mutação 1:04:41 nossos experimentos iniciais foram feitos em células hek293t 1:04:48 tentamos reproduzir a mutação de mx1g e direcionar 1:04:55 dmd exon 35. então, essencialmente, essas células foram transfectadas 1:05:01 com codificação de plasmídeo para o cas9 djs se funde com os dias de transmissão reversa 1:05:07 e um rna pago visando o exon 35 do gene dmd 1:05:13 ou o e mx1 g o dna foi extraído três dias depois 1:05:20 e a sequência alvo foi amplificada por pcr e sequenciada usando o método central 1:05:26 a sequência foi analisada usando o programa online edit r essencialmente observamos 1:05:34 uma mutação de correção de 32 por cento do gene air x1 tem 1:05:41 feito por heads along, no entanto, para a mutação do exon 35 1:05:48 tivemos um fundo de dois por cento na sequência do controle negativo 1:05:55 controle e com os diferentes peg rna temos mutação variando de quatro a oito 1:06:02 por cento, então isso não foi tão bom quanto para o emx one g 1:06:13 acabamos de tentar um método diferente para tentar aumentar a porcentagem de edição do genoma 1:06:18 do exon 35. o primeiro método que tentamos é repetir o tratamento três vezes 1:06:26 essencialmente as células foram transfectadas com plasmídeo no 0 6 12 1:06:32 e o DNA foi extraído três dias e seis dias após cada tratamento 1:06:40 amplificamos o exon 35 pcr em cada uma das extrações 1:06:46 data e sequencia por centro e sequência do analisador como você pode ver 1:06:52 a porcentagem de edição do genoma aumentou do dia 3 para o dia 18 com o 1:06:59 tratamento e este foi o caso de todas as três redes peg rna visando o exon 35. 1:07:11 testamos então um segundo método para tentar aumentar a porcentagem de mutação no exon 35. 1:07:18 é para induzir um segundo corte no alvo g este é o método pe3 1:07:25 essencialmente, identificamos duas sequências pam que permitiram ao kite rna induzir 1:07:32 um segundo corte em 57 nucleotídeos do original 1:07:40 grande ironia vizinha 1:07:54 24 horas nucleares ou a 57 nucleotídeos induzidos pelo porco 1:08:02 houve um aumento significativo na adição da propaganda do gene alvo 35 1:08:09 quatro e figura oito por seis, mas não para maior apenas 20,5 1:08:15 você ainda tem que entender por que 1:08:22 i método para melhorar a porcentagem de mutação no gene alvo é mutar 1:08:29 o pam usado pela harmonia de peg 1:08:36 acabamos de projetar rna de porco que não só foi capaz de introduzir um códon de parada 1:08:43 mutação, mas também somos capazes de mutar simultaneamente 1:08:48 a panela e o uso 1:08:54 mutação do pan usado pelo peg rna melhora a porcentagem de mutação em 1:09:01 o códon de parada para dois dos três peg rna que nós 1:09:06 testei 1:09:12 combinando os dois métodos que estão induzindo um segundo corte no alvo g 1:09:19 e a mutação do pan usado pelo peg rna aumenta ainda mais a mutação do dmd 1:09:26 exon 35 a 39 com todos os três pinos que temos 1:09:32 testado 1:09:41 estamos atualmente iniciando um novo projeto para corrigir a mutação responsável por outros títulos constantes 1:09:47 doença estamos trabalhando na fibrose cística devido a mutação no canal de cloreto cftr 1:09:55 na distrofia muscular congênita por mutação no receptor da reanodina e na 1:10:02 ataxia 8 devido a mutação no nkx6 1:10:07 gene tipo 2 1:10:13 para cada doença auditiva estável devido a uma mutação pontual, por exemplo, aqui com ataques em 1:10:19 tipo 8 é possível corrigir em princípio o gene mutado usando a edição prime 1:10:26 tecnologia neste caso aqui podemos identificar que a mutação é uma mudança de adenosina para o tempo 1:10:34 e assim podemos identificar um pan ng para o sp cas9 que está próximo do mutante 1:10:40 nucleotídeo podemos então projetar um RNA plano que irá introduzir a mutação desejada neste 1:10:47 caso estamos introduzindo duas mutações, uma para corrigir a mutação 1:10:53 reverter a timodina em adenosina e 1:10:58 a segunda mutação do ponto médio é modificar o caminho para que, seguindo o 1:11:03 correção a enzima catiônica não pode mais se ligar ao dna 1:11:13 tecnologias derivadas de cassinos mais nítidas não podem ser usadas para tratar muitas cidades diferentes 1:11:18 doenças o principal problema permaneceu a inibir a entrega dos agentes de edição 1:11:27 Obrigado pela sua atenção 1:11:35 ok obrigado professor jax vou aproveitar a vez para fazer um comentário geral para quem 1:11:44 quem não fala uh quem não fala inglês ok obrigado pela sua 1:11:49 apresentação obrigado de [Música] 1:12:00 [Música] 1:13:17 eu 1:14:04 [Música] 1:15:29 [Música] 1:15:43 [Música] 1:15:52 [Música] 1:16:08 [Música] 1:16:32 esqueceram 1:16:59 [Música] 1:17:42 esqueceram 1:17:51 [Música] 1:17:57 [Música] 1:18:10 uma música] 1:19:25 ele resume o seu discurso ok não a música 1:19:39 sim senhor muito obrigado pela tradução do meu resumo em português 1:19:47 okay um 1:20:02 esqueceram 1:20:25 [Música] 1:20:30 é 1:21:12 gabriel 1:21:39 obrigado por me receber uh vamos ver se podemos começar 1:21:52 sim uh você pode ver oi meu nome é e hoje eu estarei discutindo 1:21:58 a detecção de estrelas usando tecnologia de cristal nomeou o teste que temos 1:22:03 desenvolvimento e os estudos do Hospital do dr tremblay confirmaram que muitos indivíduos infectados com 1:22:10 vírus terra ob2 ou portadores assimétricos 1:22:15 você não pode ouvir ainda não sim você pode ouvir 1:22:23 não, apenas talvez você deve falar 1:22:31 ok, eu posso realmente tentar transmitir de outra maneira, se for esse o caso, então 1:22:50 ok 1:23:02 oi meu nome é gabriel lamot e hoje estarei discutindo a detecção de cyrus kovi 1:23:09 sim isso é muito melhor é o som melhor agora e2 usando tecnologia crispr oh perfeito 1:23:14 nomeadamente o teste que temos vindo a desenvolver nos estudos de laboratório do dr trombley confirmaram que muitos 1:23:20 indivíduos infectados com o vírus osiris-cov2 são portadores assintomáticos do vírus 1:23:26 isso é problemático, pois a pandemia pode estar crescendo sem supervisão adequada, simplesmente concentrando os testes em 1:23:32 indivíduos com sintomas em oposição a populações inteiras não é suficiente 1:23:37 para melhor conter o vírus até que uma distribuição em larga escala de uma vacina eficaz esteja em andamento em larga escala e 1:23:43 teste contínuo é obrigatório o pipeline de diagnóstico atual para 1:23:49 detectar sars cov2 é um processo de três etapas, o primeiro passo é obter swabs nasofaríngeos de 1:23:56 pacientes o próximo passo é isolar o rna total das referidas amostras e fornecer o rna necessário para isso 1:24:03 terceiro passo, que é usar máquinas de videogravador quantitativo em tempo real, o rna é primeiro transcrito inversamente 1:24:10 em dna e, em seguida, amplificado, um corante é adicionado à reação de amplificação para sinalizar a presença de dna 1:24:15 fitas após um certo número de ciclos de amplificação, um resultado positivo dará 1:24:20 um sinal forte o suficiente para que a máquina o sinalize como contendo o vírus original agora esse processo é problemático para um 1:24:28 algumas razões, a primeira é que as máquinas de PCr em tempo real são extremamente caras 1:24:33 a maioria pode variar de quinze mil dólares americanos a mais de noventa mil dólares americanos 1:24:40 dado que é um equipamento bastante especializado e que nem todos os laboratórios de biologia molecular precisam de um 1:24:46 junto muito bem com uma máquina de pcr regular que custa muito mais razoáveis 5000 dólares americanos 1:24:52 como tal teste generalizado para os coronifiers usando essas máquinas não é ideal 1:24:57 adquirir o grande número de máquinas necessárias para testes generalizados é uma façanha por si só 1:25:03 e é provavelmente um dos fatores que contribuem para os longos tempos de espera por resultados 1:25:09 muitos relatos afirmaram que pode levar de 3 a 24 horas ou mais para obter resultados em uma clínica 1:25:15 laboratório de diagnóstico aqui no Canadá ontário relata tempos de espera de até quatro dias para obter resultados 1:25:22 áreas metropolitanas de alta densidade, como Nova York, também estão sujeitas a longas filas para testes e, em seguida, um tempo para 1:25:29 resultados de cerca de sete dias para algumas clínicas daquela cidade a criação de novos tipos de testes de detecção 1:25:36 é, portanto, um passo importante para conter a propagação deste vírus, um teste ideal precisa seguir o mundo 1:25:43 os critérios da organização de saúde para garantir que é o teste precisam ser acessíveis 1:25:48 para o maior número possível de pessoas em risco de infecção testes que exigem reagentes ou máquinas extremamente caras 1:25:55 não são ideais o teste também deve ser específico para evitar falsos negativos dessa forma qualquer pessoa 1:26:01 quem poderia espalhar o vírus pode ser identificado e colocado em quarentena o teste deve ser sensível para 1:26:06 que poucas pessoas que não têm o vírus são rotuladas erroneamente como tendo e tratadas inadequadamente 1:26:12 O teste também deve ser amigável ao usuário, ou seja, deve ser simples de executar e deve ser rápido e robusto 1:26:18 ou seja, deve dar um tempo aos resultados que seja rápido o suficiente para aproveitar ao máximo os resultados 1:26:23 situações em que pode levar até sete dias para obter resultados estão claramente longe do ideal 1:26:29 vez que o paciente recebe a informação que pode ter infectado muitos outros 1:26:34 os testes devem ser livres de equipamentos tanto quanto possível testes que exigem muitas máquinas raras e caras não são ideais para muitos 1:26:41 países, finalmente, o teste deve ser entregue a quem precisa 1:26:48 a descoberta do cast 13 ou c2 c2 foi revolucionária no campo da detecção molecular 1:26:54 este efetor crispr classe 2 tipo 6 é semelhante à proteína lançada 9 fora de 1:27:00 qual terminação base e terminação prime foram projetadas esta proteína também é um membro da família crispr 1:27:06 ao contrário do cas9, no entanto, o cast 13 pode ser programado para direcionar rnas em oposição a dnas 1:27:13 ligando-se ao seu molde crispr rna 13 é preparado para direcionar sequências de rna extremamente específicas após localizar um alvo 1:27:20 sequência a proteína cast 13 é ativada, isso faz com que a proteína comece a clivar 1:27:26 tudo ao seu redor em um evento chamado clivagem colateral ele cliva seu alvo original 1:27:32 e, em seguida, passa a começar a clivar todos os pesquisadores de rnas ao redor perceberam que isso 1:27:37 clivagem colateral poderia ser usada para transformar a proteína em um interruptor para um teste de detecção uma vez 1:27:43 a molécula alvo está presente o interruptor é acionado o cas13 ativado e todos os rnas circundantes são degradados por 1:27:51 marcando certos rnas na solução com uma molécula fluorescente e um supressor 1:27:56 seria, portanto, possível resolver um sinal que os pesquisadores começaram a desenvolver 1:28:02 um teste de detecção baseado nesta proteína para vírus, bactérias e doenças humanas, como câncer 1:28:09 no entanto, eles logo notaram que havia certas limitações para a proteína e que seu limite de detecção estava longe de ser 1:28:14 sensíveis o suficiente para suas necessidades recentemente, alguns testes foram projetados usando apenas cast 13 1:28:21 no entanto, esses testes são menos sensíveis e tendem a usar uma proteína cast 13 diferente 1:28:27 pesquisadores do amplo instituto decidiram complementar a proteína com algumas outras que amplificariam a 1:28:32 direcione o rna para este fim dr zhang e sua equipe criaram um novo teste chamado de alta sensibilidade específica 1:28:39 desbloqueio de repórter enzimático ou sherlock para abreviar este teste é baseado 1:28:45 na transcrição reversa do rna alvo em dna depois o dna é amplificado em um 1:28:50 temperatura constante usando um processo chamado amplificação da polimerase recombinase 1:28:56 esta técnica amplifica uma pequena quantidade de dna a uma temperatura constante ao contrário do pcr mais comumente usado 1:29:03 a incorporação desta etapa também significa que o teste de detecção que se segue pode direcionar o dna desde que a reação rpa 1:29:10 simplesmente amplifica uma determinada seção de dna usando dois primers, a sequência genética inicial pode 1:29:16 ser rna ou dna, desde que as enzimas transcriptase reversa estejam presentes para o rna 1:29:24 as sequências amplificadas são então transcritas usando uma t7 rna polimerase para criar grandes quantidades do alvo 1:29:30 rna isso permite que o cas13 tenha um pool muito maior de moléculas-alvo 1:29:36 que pode ativar a enzima uma vez que a enzima está ativa, ela faz o que discutimos antes e 1:29:42 começa a clivar todos os rnas circundantes incluindo os rnas repórter que emitem o sinal facilmente detectável 1:29:48 que faz o teste funcionar em sua versão inicial do sherlock test dois repórteres diferentes 1:29:55 moléculas foram usadas o primeiro usou uma molécula fluorescente, bem como um supressor 1:30:00 e foi capaz de produzir muita fluorescência após a clivagem do rna o outro 1:30:08 foi projetado para interagir com alguns anticorpos e quando foi clivado apareceu como um 1:30:13 segunda banda em uma tira que era bastante semelhante a um teste de gravidez 1:30:18 embora esse teste tenha sido bom em muitos aspectos, ele teve algumas desvantagens no início da pandemia, tentamos replicá-lo e 1:30:25 imediatamente teve alguns problemas, o maior problema de longe foi que alguns dos materiais necessários para o teste 1:30:30 para trabalhar só estavam disponíveis em oferta extremamente limitada os kits necessários para realizar rpa 1:30:36 reações, por exemplo, levaram aproximadamente dois meses para chegar e mesmo assim só recebemos o suficiente 1:30:41 materiais para realizar 200 testes, isso claramente não seria suficiente para produzir testes suficientes no 1:30:47 futuro, além disso, o repórter que usou uma tira estilo gravidez foi notável e parecia ser muito 1:30:54 útil no entanto, uma vez que era muito difícil adquirir quantidades insuficientes 1:30:59 decidimos não usá-lo e, em vez disso, concentrar nossos esforços no uso do repórter de estilo fluorescente rna desde a versão original 1:31:07 do teste não pôde ser usado por nós da maneira que se pretendia, decidimos redesenhá-lo 1:31:14 ao redesenhar o teste tínhamos várias opções e caminhos que podíamos seguir sabíamos que queríamos continuar usando 1:31:20 cast 13 porque tínhamos um grande suprimento dessa enzima devido a uma colaboração contínua com o dr 1:31:26 alain Yani também sabíamos que queríamos a todo custo manter a natureza isotérmica do 1:31:32 neste teste uma das maiores vantagens do sherlock foi que ele não exigia grandes quantidades de equipamentos caros 1:31:38 simplesmente usando um bloco de aquecimento ou algo do tipo era possível obter uma leitura visual 1:31:44 decidimos, portanto, empregar amplificação isotérmica mediada por loop ou lâmpada para encurtar essa amplificação 1:31:51 estratégia foi bastante bem documentada e fácil de executar com base no uso de seis primers 1:31:57 esta técnica pode amplificar rapidamente grandes quantidades de dna alvo, ao contrário de rpa e pcr, no entanto, a lâmpada 1:32:03 não cria amplicons idênticos de tamanho discreto, em vez disso, os seis primers podem interagir para 1:32:09 criar moléculas muito maiores de uma sequência de repetição inicialmente era um pouco difícil 1:32:15 incorpore essa estratégia de amplificação isotérmica em nosso teste, pois você pode se lembrar da etapa seguinte 1:32:21 rpa no teste sherlock original foi aquele que produziu muitos e muitos rna alvo 1:32:27 essa produção de rna alvo só foi possível porque a etapa rpa adicionou uma tag que deixou o rna t7 1:32:33 polimerase se liga ao dna e começa a transcrevê-lo, no entanto, ninguém aparentemente nunca fez 1:32:40 que com lâmpada e como essa nova técnica usou seis primers, dois dos quais se enrolaram para criar 1:32:45 estruturas estranhas semelhantes a halteres, era difícil descobrir exatamente onde incorporar essa tag 1:32:52 depois de um tempo, decidimos incluir a tag bem no meio de um de nossos primers de loop, isso tem sido consistentemente 1:32:59 dado resultados muito fortes, fomos capazes de adaptar o sherlock original 1:33:04 teste com uma nova estratégia de amplificação enquanto ainda se beneficia da especificidade e sinalização do cast 13 1:33:12 o novo teste está, portanto, usando rt lamp em vez de rt rpa, é claro 1:33:18 devemos nos interessar em direcionar o DNA no futuro para certos tipos de vírus ou 1:33:24 certas bactérias este teste seria prontamente aplicável a isso também decidimos usar um fluorescente 1:33:30 repórter rna em vez do estilo de gravidez de que falamos anteriormente porque parece ser o mais prontamente 1:33:37 material disponível, uma vez que não é necessário nenhum maquinário particularmente avançado para fazê-lo funcionar 1:33:42 ficamos felizes em escolher este 1:33:48 agora que você sabe como o teste funciona do ponto de vista teórico, vamos discuti-lo de um ponto de vista mais prático por enquanto 1:33:54 o teste requer que comecemos com rna que foi extraído de um vírus usando um kit comercialmente disponível 1:34:00 microlitro desta solução é transferido para o tubo contendo a reação da lâmpada rt 1:34:06 idealmente, no futuro, gostaríamos de modificar o teste para que seja possível adicionar diretamente a saliva de um paciente 1:34:12 a ele e continuar a partir daí, o que reduziria visivelmente o trabalho necessário para obter cada leitura 1:34:18 reduzir o custo geral e tornar muito mais rápido os resultados 1:34:23 depois de transferir um microlitro do extrato de rna para o primeiro tubo, o tubo deve ser incubado a 65 1:34:29 graus Celsius por 30 minutos depois que um microlitro é transferido do primeiro tubo para o segundo 1:34:36 que contém a solução de t7 e 13 depois de bater no tubo algumas vezes para 1:34:42 misture e microcentrifugue por alguns segundos tudo o que você precisa fazer é incubar esse tubo a 37 graus Celsius 1:34:49 por 30 minutos nesse ponto todas as reações são feitas e que os resultados estão prontos para serem 1:34:54 ler expondo os tubos a um comprimento de onda de aproximadamente 490 nanômetros é possível facilmente 1:35:00 detectar quais amostras contêm cyrus kov2, essas irão fluorescer um verde brilhante 1:35:07 aqueles que não continham nenhum dos espécimes virais de interesse serão completamente incolores e 1:35:12 indistinguível de um tubo cheio de um pouco de água eu vou te mostrar isso mais tarde 1:35:18 agora vale a pena notar que as sequências de dna e rna que usamos nesta primeira versão do nosso teste 1:35:23 foram todos publicados anteriormente por diferentes grupos, como tal, não acreditamos que eles 1:35:28 resultar em um sinal positivo quando na presença de um rna relevante 1:35:33 isso é particularmente importante porque sua saliva está cheia de rna o processo de extração do vírus 1:35:40 de fato resulta na captura de rnas virais, mas tende a haver muito mais 1:35:45 rnas humanos e bacterianos, além de outros coronavírus que são 1:35:51 muito menos perigosos são bastante comuns na população humana se nosso teste deu sinais positivos toda vez que alguém entrou 1:35:57 com um resfriado comum, não seria muito eficaz, pois nos baseamos em 1:36:02 modelos descritos anteriormente para tentar evitar isso o máximo possível 1:36:08 ao projetar este teste, tentamos garantir que ele não dependesse excessivamente de máquinas complicadas 1:36:14 queríamos que todo o teste fosse fácil de realizar usando apenas alguns aparelhos comuns de laboratório 1:36:20 como resultado, com esta iteração atual do teste, tudo o que precisamos é de uma máquina que possa aquecer 1:36:25 tubos estilo pcr a 65 graus celsius e um que pode aquecer 1:36:30 os tubos pcr a 37 graus celsius também precisamos de dois p2 ou p10 1:36:37 pipetas por motivos que abordaremos mais tarde, juntamente com suas pontas de pipeta associadas 1:36:43 uma pequena microcentrífuga capaz de receber tubos de PCr também é necessária apenas para garantir que a reação 1:36:49 misturas não tocam no topo do tubo quando você os abre e potencialmente contaminam todos os 1:36:55 tubos circundantes, finalmente, é necessária uma máquina capaz de emitir comprimentos de onda ultravioleta 1:37:02 nesta imagem você verá a máquina que tenho usado é mais comumente usada para visualizar géis em uma biologia molecular 1:37:08 lab, mas faz um trabalho muito bom ao visualizar nossas amostras positivas em nosso teste para as duas incubações 1:37:15 períodos várias opções diferentes estão disponíveis eu tenho usado um termociclador antigo hoje 1:37:21 como eu acho que ele faz um bom trabalho de aquecimento uniforme dos meus tubos, vale a pena notar aqui que isso significa 1:37:26 que mesmo termocicladores antigos e degradados que não fazem mais um bom trabalho de ciclismo entre temperaturas 1:37:32 pode ser prontamente usado neste teste, ao contrário do padrão ouro rtq pcr atual que requer 1:37:40 termocicladores especializados em tempo real aqui qualquer máquina antiga pode ser usada 1:37:45 também é possível usar outros aparelhos comuns de laboratório, como aquecedores de bloco que têm um 1:37:51 adaptador para tubos pcr por favor note que nesta foto o aquecedor do bloco tem um adaptador para 1,5 1:37:57 tubos de microcentrífuga milimétricos para que o verdadeiro adaptador pareça um pouco diferente 1:38:03 também usei incubadoras com grande sucesso, mesmo incubadoras de materiais que operam em um 1:38:08 37 graus Celsius podem atender perfeitamente às necessidades deste teste, desde que os tubos sejam prontamente expostos 1:38:15 à temperatura ambiente, os sinais positivos não devem ter dificuldade em resolver 1:38:20 observe, no entanto, que ao usar incubadoras, é melhor ter os tubos expostos ao ar 1:38:25 assim eles não perdem tempo enquanto o rack começa a esquentar lentamente 1:38:31 os banhos de água são uma opção final que pode escolher pessoalmente, tendo a tendência de evitar esta opção 1:38:36 porque acho que o risco de contaminação cruzada entre amostras é muito maior e, portanto, não ideal 1:38:43 no entanto, tentei realizar reações de lâmpada rt com este sistema e desde que você esteja 1:38:48 cuidado é muito possível fazê-lo 1:38:53 uma vez concluídas as reações, é possível usar várias máquinas diferentes para visualizar os tubos 1:38:59 dependendo dos materiais que seu laboratório tem pessoalmente, minha máquina de escolha é um gel 1:39:04 emissor uv essas máquinas que são mais comumente usadas para visualizar géis de agarose 1:39:09 fazer um trabalho muito bom de mostrar com segurança quais tubos são fluorescentes e quais não são luzes negras também podem 1:39:16 ser usados para este teste, no entanto, achei-os um pouco menos desejáveis, pois o repórter rna absorve melhor 1:39:23 comprimentos de onda de 490 nanômetros, descobri que as luzes negras que produzem comprimentos de onda de 390 nanômetros 1:39:30 para ser menos favorável para este teste para eles funcionarem é melhor visualizar os tubos em um quarto escuro 1:39:37 em ambos os casos a máquina deve realmente ser colocada em uma sala mais escura longe da luz excessiva um pouco 1:39:43 a luz de fundo parece ter menos efeito no caso da luz uv em gel, no entanto 1:39:48 esta foto vista à esquerda foi tirada usando um iphone genérico quando os tubos foram colocados no gel uv 1:39:55 acender as luzes da sala foram apenas parcialmente desligadas, resultando em muita iluminação ambiente 1:40:01 mesmo que não houvesse luzes apontadas diretamente para a máquina, dada a radiação forte e uniforme que os tubos 1:40:07 recebido nesta máquina é fácil determinar quais amostras foram positivas e quais foram negativas 1:40:14 no caso da luz negra à direita fica claro quais amostras são positivas e quais são negativas 1:40:19 claro, no entanto, a fluorescência não é uniforme e é um pouco mais difícil de detectar 1:40:24 a olho nu, neste caso, a câmera do iphone tirou uma foto muito boa 1:40:29 e tornou mais fácil visualizar os tubos em geral, agora existem vários importantes 1:40:35 considerações a serem feitas ao usar este teste para que ele funcione corretamente e não dê falsos positivos ou falsos 1:40:41 negativos, é importante primeiro designar estações de trabalho adequadas para cada seção do teste. 1:40:48 necessário seguir os tempos de reação predeterminados sem variar, caso contrário os resultados podem começar a diferir 1:40:54 um pouco finalmente quem manuseia o teste deve ter cuidado para não contaminar nenhum dos tubos com 1:41:00 rnase a primeira consideração para separar as áreas de trabalho 1:41:06 é extremamente importante porque o cordeiro é excessivamente sensível esta técnica é conhecida por produzir lotes 1:41:12 e muito DNA alvo concentrado nós, assim como outros, notamos que 1:41:17 quando abrimos tubos que completavam a amplificação da lâmpada na mesma área que originalmente usamos 1:41:23 para preparar a reação é possível contaminar a área de trabalho com aerossóis contendo o 1:41:28 produto se você continuar a configurar as reações da lâmpada nessas áreas depois, corre o risco de 1:41:34 contaminando seus novos tubos com amplicons das reações anteriores, tocando sua mesa ou 1:41:40 várias outras superfícies contaminadas com suas luvas, você corre o risco de semear artificialmente sua reação 1:41:46 misturas que contêm rna do paciente sem sars cov2 e, portanto, produzindo resultados positivos 1:41:52 quando realmente não deveria haver nenhuma separando as áreas nas quais você configura as reações da lâmpada 1:41:58 e aqueles em que você usa as sequências amplificadas corre menos risco de isso acontecer 1:42:04 também é necessário ter pipetas designadas para jalecos e outros materiais para cada 1:42:09 estação de trabalho se aqueles na estação de trabalho 2 forem contaminados, você não quer que isso aconteça 1:42:14 de volta à estação de trabalho 1. observe que isso é muito menos rigoroso ao trazer materiais de 1:42:20 estação de trabalho 1 para estação de trabalho 2. já que é a reação da lâmpada rt que 1:42:25 corre o maior risco de contaminação trazer material por exemplo luvas 1:42:30 dessa estação para a próxima não deve ser um problema, desde que as luvas ainda estejam 1:42:35 relativamente limpo, observe que esta situação de contaminação por aerossol 1:42:42 é de muito menos importância durante a segunda etapa do teste, pois discutimos anteriormente o cas13 1:42:48 proteína que estamos usando requer uma quantidade relativamente grande de rna para ser funcional 1:42:53 no momento, não estamos nem um pouco preocupados que uma contaminação por aerossol da lâmpada 1:42:59 pode produzir falsos positivos de nossas reações do elenco 13, pois ainda temos que ver uma única situação 1:43:05 onde isso aconteceu, a segunda consideração digna de nota é que 1:43:10 o tempo de reação deve ser seguido uma pequena discrepância pode ser tolerada que seja um minuto a mais ou a menos não 1:43:18 realmente parecem ter um grande impacto no teste, no entanto, mais do que isso pode começar a se tornar problemático 1:43:24 no caso das equipes externas de reação à lâmpada rt, assim como nós vimos que dobrando a reação 1:43:30 tempo para a lâmpada podem surgir falsos positivos como você pode ver aqui em ambas as fotos 1:43:36 uma reação bem-sucedida da lâmpada também pode ser visualizada em um gel de agarose, as reações bem-sucedidas são 1:43:43 caracterizada pela presença de várias bandas grandes de tamanhos variados, no entanto, quando a lâmpada 1:43:49 as reações continuam por muito tempo é possível começar a amplificar amostras sem nada nelas 1:43:54 por exemplo à esquerda você verá um gel que foi retirado de um artigo no qual em 30 minutos os poços 1:44:01 contendo reações com 10 cópias do alvo são RNA viral e nenhuma cópia do 1:44:06 o rna viral alvo não tinha bandas no caso do gel à direita um gel que fiz três dos poços 1:44:13 continha reações que não tinham rna alvo para falar apenas do fragmento n bem contido 1:44:20 rna alvo em 30 minutos esses controles negativos não demonstraram qualquer amplificação 1:44:26 como esperávamos, no entanto, em 60 minutos, tanto o gel publicado quanto o meu começaram 1:44:32 para dar produtos amplificados em seu caso as cópias 10 e 0 ambos 1:44:37 começou a ser amplificado e no meu caso uma das minhas amostras negativas começou a ser amplificada eu realizei 1:44:45 vários experimentos até agora com tempos de incubação de 30 minutos e até agora nunca obtiveram falsos positivos 1:44:53 para não dizer que é totalmente impossível, simplesmente que é muito, muito improvável 1:44:58 como nota lateral, este é um bom momento para mencionar que trocar as luvas com frequência ao realizar a primeira reação é um 1:45:05 boa maneira de evitar esse tipo de falsos positivos improváveis após uso prolongado 1:45:10 luvas podem ficar contaminadas com pequenas quantidades de RNA viral e isso pode levar a 1:45:15 positivos mesmo se estivermos incubando apenas em 30 minutos 1:45:20 a consideração final a ser observada é a presença de rnases para aqueles de vocês que podem não estar 1:45:26 rnases familiares são enzimas que clivam todos os rnas que encontram 1:45:31 ambas as etapas para este teste são sensíveis a rnases a lâmpada arty inicial começa sua 1:45:36 amplificação do rna, de modo que a presença de rnases pode ser muito prejudicial e, portanto, 1:45:42 levar a falsos negativos o segundo passo do teste o t7 e o cast 13 passo usa um rna 1:45:49 repórter para sinalizar tubos positivos se enquanto você estiver usando os testes você começar a introduzir rnases 1:45:55 então você corre o risco de obter falsos positivos rnases são extremamente difíceis de remover 1:46:01 uma vez que eles são introduzidos em um sistema, então o melhor meio de proteger seu teste é usando a prevenção 1:46:06 uma vez que as suas mãos produzem muitos rnases é obrigatório o uso de luvas sempre ao trabalhar com o teste 1:46:13 ao fazer isso, você evitará que as rnases naturais do seu corpo degradem as estrelas iniciais cov2 1:46:18 rna e proteger o repórter fluorescente no final as luvas também devem ser trocadas sempre que 1:46:23 eles entram em contato com o cabelo da pele ou outros objetos frequentemente manipulados 1:46:29 como maçanetas e dispositivos pessoais o uso de rnas e dnase free 1:46:36 pipetas filtradas também é importante para este teste usando esses tipos de pontas especializadas 1:46:42 você pode ter certeza de que quaisquer possíveis contaminações que você possa ter em suas pipetas não tenham chance 1:46:48 contaminar seu teste em áreas onde o risco de contaminação por rnas é bastante alto, pode ser 1:46:54 vale a pena tratar todas as superfícies ou ferramentas com uma solução de remoção de rnas 1:46:59 esses tipos de soluções podem degradar rnases que poderiam grudar nas luvas e contaminar suas amostras 1:47:06 por favor, note que eu não tive que usar a solução com muita frequência, desde que você mantenha um trabalho limpo 1:47:13 agenda você deve estar bem o segundo componente para o teste o que contém t7 e cast 13 é 1:47:21 também projetado para ser capaz de tolerar um certo nível de rnases contaminantes, há um inibidor de rnas adicionado ao 1:47:28 mistura de reação para evitar a degradação do repórter no caso do sars kobe 2 rna original 1:47:35 não estava completamente limpo ou no caso de ocorrerem contaminações enquanto você estava reparando os testes 1:47:41 que disse que a presença de rnases excessivos ainda pode ativar totalmente o teste visto 1:47:48 aqui à direita um microlitro de rnase a muito concentrada é capaz de fazer com que o tubo de ensaio 1:47:54 tornar-se fluorescente, portanto, é importante levar a 1:48:02 requerido 1:48:16 cabriolé 1:48:26 teste que pode ser amplamente distribuído e, ao mesmo tempo, atender a esse limite de detecção, é totalmente funcional para conter a 1:48:34 propagação desta pandemia enquanto rtq pcr é muito mais sensível 1:48:39 do que isso, sua detecção limitada aprimorada pode não ser necessariamente tão benéfica 1:48:44 uma vez que esta técnica pode recolher rnas libertados por células infectadas e mortas após a infecção ter terminado 1:48:51 essa forma de triagem pode fazer com que indivíduos nominalmente sars kovi 1:48:56 positivos, mas não são realmente infecciosos para serem isolados desnecessariamente 1:49:02 como você pode ver aqui à nossa esquerda, nosso teste de detecção é capaz de detectar amostras 1:49:07 que possuem 100 exemplares por microlitro como foi estipulado pelo modelo mais 1:49:12 comparação recente entre os diferentes primers que usamos para a lâmpada demonstrou 1:49:17 que uma versão do nosso teste pode detectar amostras contendo apenas 80 cópias por microlitro 1:49:23 enquanto o outro só pode detectar amostras contendo 1.000. no futuro, provavelmente focaremos nossa 1:49:29 esforços no primeiro conjunto de primers para garantir que atingimos o limite de detecção que foi 1:49:34 estipulado pelo modelo como nota final, temos o prazer de informar 1:49:39 que nosso teste funciona não apenas em fragmentos do genoma cyrus cov2, mas também quando exposto ao 1:49:46 perfil de rna completo do vírus inicialmente começamos o desenvolvimento de nosso teste usando fragmentos 1:49:52 dos genes de vírus que nós mesmos havíamos transcrito no laboratório recentemente, usamos o teste 1:49:59 em vírus sars cov2 reais e obtiveram os resultados esperados 1:50:04 como você pode ver à esquerda, a primeira seção da reação, a reação da lâmpada rt funciona da mesma forma 1:50:10 esperado no rna viral, os poços superiores esquerdos que foram executados no gel de agarose demonstram claramente 1:50:16 uma forte amplificação abaixo deles três reações foram realizadas com células que não haviam sido cultivadas 1:50:22 com o vírus, os rnas virais foram criados isolando primeiro os vírus de um paciente 1:50:28 esses vírus foram então cultivados em células vero e6 e após alguns dias o meio de cultura 1:50:34 foi tratado para extrair todo e qualquer rna que estivesse presente, os vírus foram, portanto, destruídos e 1:50:40 seu rna foi obtido quando os amplicons de laboratório que amplificaram o vírus real 1:50:46 foram transferidos para o segundo estágio do teste, eles deram os fortes sinais fluorescentes esperados 1:50:52 no momento o que resta a ser feito é usar nossos testes em amostras que foram confirmadas positivas ou 1:50:58 negativo por rtq pcr o padrão ouro atual na detecção de sarsko v2 1:51:05 e ver como nosso teste se compara isso nos dará uma melhor indicação de qual é a sensibilidade de nossos testes e 1:51:11 especificidade são apenas para encerrar gostaria de agradecer ao dr gary cobinger 1:51:17 dr alain ghani e dr ghiblave por terem ajudado a fornecer recursos financeiros ou materiais 1:51:23 para este projeto eu também gostaria de agradecer ao dr tremblay e a todos em sua equipe por terem ajudado a fornecer algumas 1:51:29 insights como eu estava redesenhando este teste finalmente eu gostaria de agradecer ao dr marcelo por 1:51:35 tendo ajudado a organizar todo este encontro e o instituto canadense de pesquisa em saúde 1:51:40 e os frqs por terem me ajudado a me financiar enquanto eu seguia este projeto 1:51:50 ok então essa foi minha apresentação uh sim 1:51:58 obrigado gabriel uh eu vou tomar o tempo apenas para fazer um para resumir o melhor que posso aqui para 1:52:05 os que não falam inglês muito obrigado pela apresentação obrigado ok então 1:52:13 [Música] 1:52:34 [Música] 1:52:40 [Música] 1:53:10 é 1:53:24 é 1:54:06 esqueceram 1:54:20 positivo 1:54:50 [Música] 1:55:34 [Música] 1:56:06 [Música] 1:56:30 [Música] 1:56:41 [Música] 1:57:04 [Música] 1:57:32 [Música] 1:57:38 obrigado matilda e obrigado dr graviol 1:57:44 professor jackson você gosta de falar algo neste momento uh eu não tenho nada a acrescentar 1:57:50 exceto se houver alguma pergunta que eu possa responder, caso contrário agradeço por organizar esta sessão 1:58:00 obrigado pergunta 1:58:05 é uh escrevendo inglês você pode ler o comentário primeiro 1:58:11 você pode ler os comentários sim, mas eu acho que a maioria deles 1:58:17 estão em português não, pedi para você escrever em inglês i 1:58:23 tem nos comentários oh ok eu estava olhando no chat privado 1:58:34 eu estou subindo na lista oh boy muito 1:58:46 comentários 1:58:54 você está no bate-papo inicial sim, estou apenas olhando os comentários muito rapidamente 1:58:59 uh crescer anacrestia é é é a probabilidade 1:59:06 que o teste crispr dará resultados falsos negativos, essa é uma pergunta principalmente para gabrielle gabriel 1:59:14 você pode responder isso uh, então no momento não 1:59:20 sei com meu teste geralmente hum 1:59:25 testes semelhantes a este têm uma sensibilidade de cerca de 90 por cento, então a probabilidade de dar 1:59:32 um resultado negativo é muito baixo porque também tende a ter uma sensibilidade de cerca de 80 a 90, então no geral é melhor 1:59:41 do que algumas das alternativas que existem que não são rtq bcr outra pergunta para 1:59:46 você também é da anna christina faz o teste mais nítido 1:59:52 aplicar a outras doenças como ebola zika ou dank 1:59:59 então, na verdade, pretendemos adaptar o teste ao ebola assim que pudermos, estamos brincando 2:00:05 com a ideia de fazer zika leps e alguns outros porque tudo o que precisamos fazer é mudar alguns dos 2:00:11 sequências que estamos usando para que os primers da lâmpada e o guia para a proteína 13 mais nítida e nesse 2:00:18 ponto, seremos capazes de começar a detectar esses vírus imediatamente, então agora que o teste existe, é apenas um 2:00:24 questão de otimizá-lo para cada vírus individual ok, há outro 2:00:30 pergunta da frança antártica nouvelle uh quais são as perspectivas de usar o crispr 2:00:35 tecnologia castline para tratar o hiv devo admitir que não sou 2:00:41 um especialista em hiv eu sei que alguns grupos estão trabalhando nisso eu não sei quais são as chances disso 2:00:48 se isso funcionará ou não, mas acho que isso é muito zonal, você conhece as bactérias 2:00:54 usam a tecnologia crispr cat9 há milhões de anos para cortar o vírus e, portanto, a ideia aqui é 2:01:02 usar a tecnologia em cascata para esmagar para cortar o vírus hiv 2:01:07 eu acho que isso é bastante notável de fato no início da pandemia do cobia 19 eu vi um grupo nos unidos 2:01:15 Estados que se propunham a usar a tecnologia crispr cast 9 2:01:21 de fato, para cortar o vírus da cópia 19, então é a mesma abordagem para o hiv i 2:01:27 acho que esta é uma abordagem razoável, meu laboratório não está trabalhando nessa abordagem 2:01:36 também desde o início, uh, essa tecnologia pode ser antibiótica em um futuro próximo para 2:01:44 exemplo para tratar a tuberculose multirresistente novamente acho que é uma boa sugestão e 2:01:52 sim, de fato, o principal problema com a tecnologia crispr cas9 2:01:58 é encontrar uma técnica adequada para entregar tanto a proteína cast 9 do 2:02:03 castline e até agora na terapia gênica o que está sendo usado é o vírus adeno associado 2:02:11 infelizmente eu não sabia que a fortuna personalizada do vírus associado para produzir 2:02:16 em boas práticas de fabricação, então temos que encontrar outro método de entrega para entregar no cas9 2:02:23 proteína ou o gene cas9 e então facilitaria o uso porque agora seria 2:02:29 apenas muito caro para ser usado em vez de um antibiótico 2:02:36 também do francês e o tactic crispr cast 9 pode ser uma opção no 2:02:42 futuro próximo para tratar a malária koben ebola zika bem, tudo isso eu acho 2:02:50 é viável se eu tivesse mais dinheiro no meu laboratório, poderíamos começar a trabalhar nisso também ii 2:02:57 acho que estes são um projeto razoável [Música] 2:03:09 [Música] muitos dos comentários estão em português 2:03:15 infelizmente não há nenhuma pergunta para você sim apenas 2:03:23 comentários sem perguntas deixe-me tentar ajudar 2:03:29 há alguma pergunta apenas comando sim 2:03:38 vejo que vario entre duas e cinco estrelas 2:03:46 bem uma pergunta do vitor é gostaria de saber é gostaria de saber se 2:03:52 crispr é acessível ao sistema público de saúde e se pode contribuir para o custo 2:03:59 redução da terapia genética que já existe 2:04:05 a principal causa de terapia gênica que existe atualmente é a produção do adenocarcinoma 2:04:11 vírus associado em condições de boas práticas de fabricação na última vez em que penso em fazer um 2:04:18 ensaio clínico ou uma entrega sistêmica de alguma terapia genética 2:04:24 você levou cerca de um milhão de dólares para produzir aav suficiente para tratar um paciente para fazer 2:04:32 um ensaio clínico em 10 pacientes que você precisava apenas para iniciar um orçamento de 2:04:37 10 milhões e claro que até agora não consegui obter um orçamento tão grande uh o único 2:04:45 pessoas que têm um orçamento tão grande são empresas americanas que vão gastar uma fortuna fazendo isso 2:04:52 ensaios clínicos e eles têm milhões de dólares disponíveis, o problema é que 2:04:58 após o tratamento ter se mostrado eficaz, o custo do tratamento é de 2,3 milhões 2:05:05 dólar por pessoa, então eu acho que é o futuro que precisamos para desenvolver genes 2:05:12 terapia para muitas doenças de estudo, mas também precisamos desenvolver 2:05:17 uma terapia genética barata que você conhece ii acho que idealmente uma terapia genética deveria custar cerca de 100.000 2:05:25 nem um milhão de dólares porque a maior parte do sistema de saúde pública não pode se dar ao luxo de fazer isso eu acho que 2:05:32 é apenas nos Estados Unidos que as pessoas ricas podem pagar por aqueles 2:05:37 e os pobres não terão acesso ao tratamento 2:05:42 [Música] ainda procurando a lista para ver se há alguma outra pergunta 2:05:51 desculpe-me professor jax só para fazer um pequeno comentário aqui para 2:05:57 aqueles que não falam inglês vou tentar pegar a ideia geral das respostas que você acabou de dar e pegar 2:06:05 gabriel também uh só um segundo 2:06:10 princípio estrangeiro 2:06:21 [Música] 2:06:42 esqueceram 2:06:56 tecnologia 2:07:51 obrigado pelo seu tempo e se houver alguma dúvida, você pode continuar lendo e respondendo 2:07:59 bem, se houver outras perguntas, as pessoas sempre podem me enviar algumas 2:08:04 e-mails ok uh obrigado professor jack england 2:08:11 por este encontro maravilhoso obrigado gabrielle obrigado barbara dr barbara 2:08:19 obrigado matteo shots e espero que você tenha outro encontro como este 2:08:28 obrigado muito obrigado adeus obrigado obrigado tenha um bom 2:09:16 esqueceram







 O Projeto Brasil Sem Alergia consolidou sua trajetória de cuidado e inclusão social em 2007, quando os médicos alergistas e imunologistas Dr. Marcello Bossois e Dra. Patrícia Schlinkert iniciaram um trabalho voluntário em
O Projeto Brasil Sem Alergia consolidou sua trajetória de cuidado e inclusão social em 2007, quando os médicos alergistas e imunologistas Dr. Marcello Bossois e Dra. Patrícia Schlinkert iniciaram um trabalho voluntário em  O Projeto Brasil Sem Alergia consolidou sua trajetória de cuidado e inclusão social em 2007, quando os médicos alergistas e imunologistas Dr. Marcello Bossois e Dra. Patrícia Schlinkert iniciaram um trabalho voluntário em
O Projeto Brasil Sem Alergia consolidou sua trajetória de cuidado e inclusão social em 2007, quando os médicos alergistas e imunologistas Dr. Marcello Bossois e Dra. Patrícia Schlinkert iniciaram um trabalho voluntário em 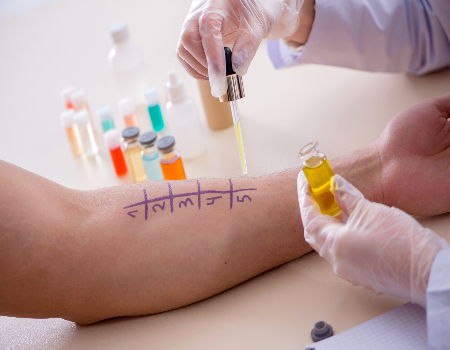 O Projeto Brasil Sem Alergia consolidou sua trajetória de cuidado e inclusão social em 2007, quando os médicos alergistas e imunologistas Dr. Marcello Bossois e Dra. Patrícia Schlinkert iniciaram um trabalho voluntário em
O Projeto Brasil Sem Alergia consolidou sua trajetória de cuidado e inclusão social em 2007, quando os médicos alergistas e imunologistas Dr. Marcello Bossois e Dra. Patrícia Schlinkert iniciaram um trabalho voluntário em  O atendimento especializado do Brasil Sem Alergia foca no diagnóstico preciso e no tratamento acessível de patologias como dermatite atópica, asma 🌬️, bronquite 🫁, rinite e prurigo estrófulo (alergia a picadas de insetos 🦟). Nossa nova unidade no Campo Limpo, em São Paulo, segue o padrão de excelência da rede, oferecendo testes para detectar alergias causadas por poeira, pelo de animais e alimentos. Como um projeto de inclusão social que complementa o
O atendimento especializado do Brasil Sem Alergia foca no diagnóstico preciso e no tratamento acessível de patologias como dermatite atópica, asma 🌬️, bronquite 🫁, rinite e prurigo estrófulo (alergia a picadas de insetos 🦟). Nossa nova unidade no Campo Limpo, em São Paulo, segue o padrão de excelência da rede, oferecendo testes para detectar alergias causadas por poeira, pelo de animais e alimentos. Como um projeto de inclusão social que complementa o 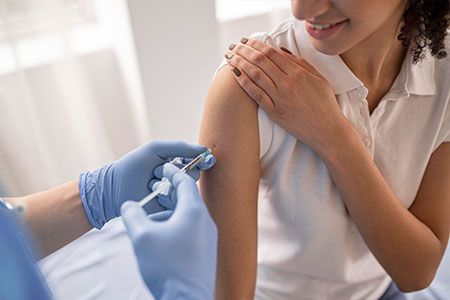 Proteja-se com Vacinas no Projeto Brasil Sem Alergia!As vacinas são uma forma segura e eficaz de prevenir doenças como gripe , febre amarela 🟡, meningite , pneumonia 🫁 e diversas alergias! O Projeto Brasil Sem Alergia oferece algumas vacinas e medicamentos gratuitos, em campanhas e com patrocínio, para ajudar você a ter mais saúde e qualidade de vida.Nossas UnidadesRio de Janeiro:
Proteja-se com Vacinas no Projeto Brasil Sem Alergia!As vacinas são uma forma segura e eficaz de prevenir doenças como gripe , febre amarela 🟡, meningite , pneumonia 🫁 e diversas alergias! O Projeto Brasil Sem Alergia oferece algumas vacinas e medicamentos gratuitos, em campanhas e com patrocínio, para ajudar você a ter mais saúde e qualidade de vida.Nossas UnidadesRio de Janeiro:  Para esta variação, o foco é a narrativa histórica e humanizada, detalhando a origem voluntária do projeto na Baixada Fluminense e sua evolução até a chegada à capital paulista. O texto está em formato corrido, otimizado para SEO e com a inclusão da unidade Campo Limpo e seus respectivos contatos.O Projeto Brasil Sem Alergia 🇧🇷❤️ é o resultado de uma trajetória de cuidado e inclusão iniciada em 2007, quando o Dr. Marcello Bossois, médico
Para esta variação, o foco é a narrativa histórica e humanizada, detalhando a origem voluntária do projeto na Baixada Fluminense e sua evolução até a chegada à capital paulista. O texto está em formato corrido, otimizado para SEO e com a inclusão da unidade Campo Limpo e seus respectivos contatos.O Projeto Brasil Sem Alergia 🇧🇷❤️ é o resultado de uma trajetória de cuidado e inclusão iniciada em 2007, quando o Dr. Marcello Bossois, médico 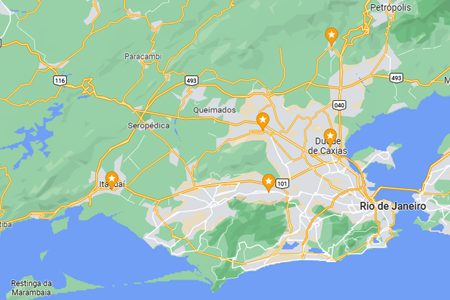 O Projeto Brasil Sem Alergia consolida sua presença nacional e expande seu alcance com unidades fixas no
O Projeto Brasil Sem Alergia consolida sua presença nacional e expande seu alcance com unidades fixas no  O Projeto Brasil Sem Alergia reforça sua missão de inclusão social através de sua unidade móvel e itinerante, que percorre diversas regiões para levar saúde e bem-estar diretamente até a sua comunidade. Com o objetivo de democratizar o acesso ao diagnóstico especializado, nossa clínica móvel oferece consulta com
O Projeto Brasil Sem Alergia reforça sua missão de inclusão social através de sua unidade móvel e itinerante, que percorre diversas regiões para levar saúde e bem-estar diretamente até a sua comunidade. Com o objetivo de democratizar o acesso ao diagnóstico especializado, nossa clínica móvel oferece consulta com 

